| 送交者: hgao[♂☆★★★★声望勋衔19★★★★☆♂] 于 2020-10-22 21:20 已读 1870 次 | hgao的个人频道 |
在生物学如此发达的今天,虽然我们已经攻克了很多疾病,可以在细胞甚至是分子的层面上对人体进行研究,甚至能够利用基因编辑的手段来改变一个生物体的性状,但是对于人体来说依旧有很多的未解之谜。
例如我们人类最关心的衰老问题,癌症问题一直都没有解决,这是两个比较大的方面,没有解决我们还能想得通。
但是要说我们现在对人体内还有哪些器官都了解的不够全面,相信你都会感觉不可思议。解剖学已经发展几个世纪了,有无数的解剖案例,怎么会不知道人体内都有啥器官呢?
其实还真是,人体是一个非常复杂的生物工程结构,可以肯定很多微小、隐藏较深的器官依旧没有被我们注意到。
这不,就在今年9月份的时候,发表在《放射性治疗与肿瘤学》杂志上的一篇论文《The tubarial salivary glands: A potential new organ at risk for radiotherapy》显示;
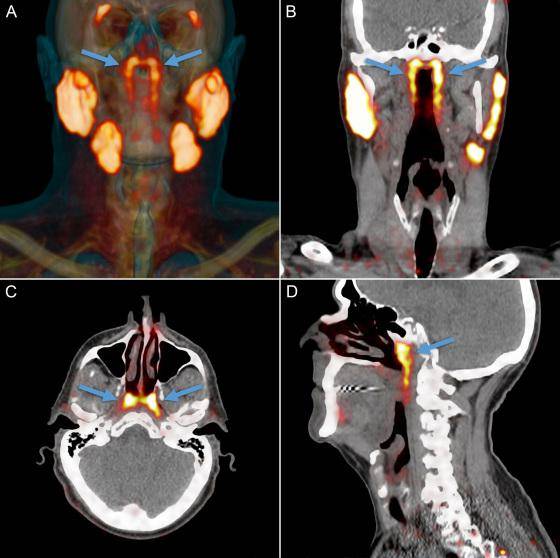
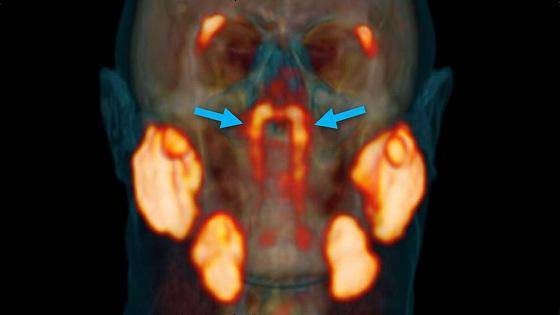
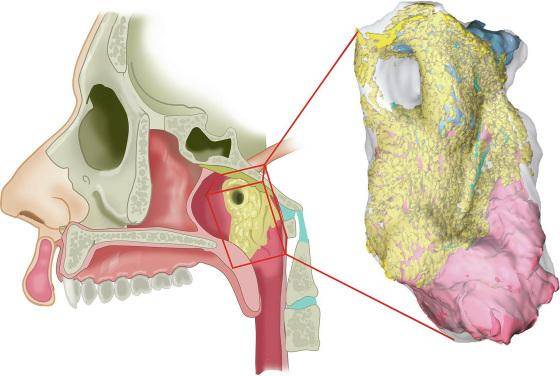
生物学家在对癌细胞的研究过程中,无意中发现了在人的鼻子到咽喉的深处有一对以前从未发现的器官,大小只有3.9公分,这个器官是唾液腺。
6park.com 这个发现让研究小组感到非常的惊喜和意外,因为我们以前认为人类有三种大唾液腺,分别为腮腺、下颌下腺、舌下腺;
除此之外还有1000个以上的小唾液腺分布在口腔和后喉咙的粘膜组织中,但从来不知道在鼻腔的后方还有一对大的、主要的唾液腺。
上图可以看出,新的器官正位于上图中箭头标注的发光的地方,其他发光的地方就是我们以前认为的唾液腺所在的位置。
那么研究人员是如何发现这个新的器官的?
研究小组起初是通过放射性示踪剂来研究前列腺癌的,这种放射性示踪剂在进入人体以后会与前列腺癌细胞中的蛋白质PSMA (前列腺特异性膜抗原)结合,这其实就是癌细胞被标记的过程。
然后通过扫描追踪放射性示踪剂我们就能知道癌细胞的位置,这种利用示踪剂成像诊断法被称为“PSMA PET-CT”。
不过PSMA这种蛋白质不仅存在于前列腺癌细胞中,在人体的唾液腺阻止中也存在,因此在扫描成像的过程中就标记出了人体中所有唾液腺的位置。
也正是通过以上的方法, 研究小组意外的发现了新的唾液腺,并且把这种新发现的器官命名为“Tubarial Glands (管状腺)”
最主要的是这个新发现的器官并非某些人特有的,研究小组随后对100名实验者进行了PSMA PET-CT,都发现了这个器官的存在,这也说明了这个器官是人体的标配。
只是我们以前没有发现,或者发现没有注意,认为它是一个无用的组织。
这个新发现对于以后治疗癌症有很大的帮助,尤其是对于头颈部癌症患者来说,因为癌症患者在接受放射性治疗的时候,放射性疗法不仅会损伤癌细胞还会杀死正常的细胞,尤其是会损害唾液腺。
造成很严重的并发症,例如唾液腺受到放射性损害以后,会造成癌症患者进食、吞咽甚至说话方面出现困难,对于癌症患者来说是一个痛苦的负担。
研究人员也分析了以往723名接受放疗的患者数据,以前在不知道这个新器官存在的时候,对这个部位进行的放疗越多, 以上的并发症就越严重,跟研究人员的猜测是一致的。
所以说发现新器官不仅惊人,而且对癌症患者是有益的,在以后的治疗中应该在技术上避开对这个新发现区域的辐射,跟避开其他唾液腺一样,这样就能保证头颈部癌症患者在接受了放疗之后降低并发症,提成治疗后的生活质量。
论文:《唾液腺:一种潜在的有放射治疗风险的新器官》
doi.org/10.1016/j.radonc.2020.09.034
评分完成:已经给本帖加上 10 银元!